Arabinos-operon
Hej!
Någon som skulle kunna förklara hur arabinos-operon fungerar? Om jag har förstått det rätt så är det i huvudsak att promotorn startar två "genavläsningar"? Men jag förstår ändå inte hur detta går till.
Det mest välbeskrivna arabinos-operonet är från E. coli. Vet du hur ett operon är uppbyggt och vad det är?
mag1 skrev:Det mest välbeskrivna arabinos-operonet är från E. coli. Vet du hur ett operon är uppbyggt och vad det är?
Jag kanske ska tillägga först att jag går på gymnasiet och läser bioteknik som ett i-val, jag går alltså inte på universitetet så har inga förkunskaper utöver biologi 1 och 2 (och första perioden av bioteknikskursen), men postade ändå tråden här eftersom man inte läser bioteknik på gymnasiet normalt sett.
Det är just arabinos-opertonet i E.coli som jag ska skriva om. Vi har gjort en laboration där man kan se att bakterier med pGLO-plasmiden lyser när de odlas på en platta med arabinos, men inte utan, vilket, om jag förstått rätt, beror på att GFP-genen aktiveras när arabinos-operonet aktiveras? Och det aktiveras när arabinos finns tillgängligt? Jag förstår dock inte om GFP-genen är en del av operonet och jag förstår inte heller hur operonet fungerar? Har jag förstått rätt om jag säger att operonet bland annat består av generna, araA, araB och araD som hjälper till vid arabinosmetabolismen (närmre behöver jag inte kunna kring de generna om det är korrekt att det är deras ansvarsområde)? Sedan läser jag att det innehåller araC, och att den aktiverar promotorn och det är här ifrån jag inte förstår.
(liten bonusfråga också, arabinosoperonet finns inte naturligt i E.coli, eller? För vi transformerade in plasmiden med arabinosoperonet)
sund20 skrev:mag1 skrev:Det mest välbeskrivna arabinos-operonet är från E. coli. Vet du hur ett operon är uppbyggt och vad det är?
Jag kanske ska tillägga först att jag går på gymnasiet och läser bioteknik som ett i-val, jag går alltså inte på universitetet så har inga förkunskaper utöver biologi 1 och 2 (och första perioden av bioteknikskursen), men postade ändå tråden här eftersom man inte läser bioteknik på gymnasiet normalt sett.
Bra att veta! Då utgår jag ifrån det.
Ett operon är en enhet av DNA som innehåller en grupp av gener, vilka kontrolleras av en gemensam promotor. Dessa gener är oftast kopplade till en gemensam funktion i cellen och de protein som generna kodar för behöver finnas i cellen samtidigt. Som i ditt exempel med arabionsoperonet där araB+araA+AraD produkterna tillsammans gör att E. coli kan utnyttja arabinos från sin omgivning.
Det finns många olika sorters operoner, med individuella funktioner (t.ex. ett annat operon för laktos).
När de strukturella generna (=de som sedan ger upphov till de respektive proteinerna) transkriberas görs detta som en lång mRNA-sträng, vilken kan användas i sin helhet, eller så kan den delas till kortare mRNA som var och en kodar för ett protein var. De andra delarna av operonet sköter regleringen med mera.
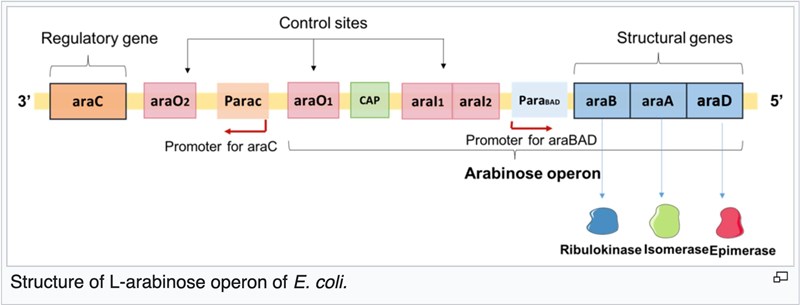
I pGLO plasmiden har endast promotorn PBAD (eller ParaBAD i bilden) tagits från ara-operonet, inget mer. PBAD promotorn klassas som en stark promotor (=den ger upphov till mycket mRNA, och därmed mycket protein), vilket är bra för att få mycket protein eller i ditt fall rejält gröna celler.
pBAD promotorn aktiveras av arabinos precis som i naturen, och ger upphov till transkription av den efterföljande genen för GFP.
Jadå detta operon finns naturligt i E. coli kromosomen. Så när ni tillsatte arabinos aktiverades PBAD promotorn i E. coli kromosomen, så arabinos kunde användas - och den extra PBAD promotorn i er plasmid, vilket gav transkription av er efterföljande GFP gen.
Den starka promotorn PBAD togs från det naturliga operonet och stoppades in i plasmiden, på så vis fås E. coli som kan skapa GFP endast när arabinos finns tillsatt - så ni kan slå på GFP bildningen precis när ni vill genom att bara mata med arabions.
mag1 skrev:sund20 skrev:mag1 skrev:Det mest välbeskrivna arabinos-operonet är från E. coli. Vet du hur ett operon är uppbyggt och vad det är?
Jag kanske ska tillägga först att jag går på gymnasiet och läser bioteknik som ett i-val, jag går alltså inte på universitetet så har inga förkunskaper utöver biologi 1 och 2 (och första perioden av bioteknikskursen), men postade ändå tråden här eftersom man inte läser bioteknik på gymnasiet normalt sett.
Bra att veta! Då utgår jag ifrån det.
Ett operon är en enhet av DNA som innehåller en grupp av gener, vilka kontrolleras av en gemensam promotor. Dessa gener är oftast kopplade till en gemensam funktion i cellen och de protein som generna kodar för behöver finnas i cellen samtidigt. Som i ditt exempel med arabionsoperonet där araB+araA+AraD produkterna tillsammans gör att E. coli kan utnyttja arabinos från sin omgivning.
Det finns många olika sorters operoner, med individuella funktioner (t.ex. ett annat operon för laktos).
När de strukturella generna (=de som sedan ger upphov till de respektive proteinerna) transkriberas görs detta som en lång mRNA-sträng, vilken kan användas i sin helhet, eller så kan den delas till kortare mRNA som var och en kodar för ett protein var. De andra delarna av operonet sköter regleringen med mera.
I pGLO plasmiden har endast promotorn PBAD (eller ParaBAD i bilden) tagits från ara-operonet, inget mer. PBAD promotorn klassas som en stark promotor (=den ger upphov till mycket mRNA, och därmed mycket protein), vilket är bra för att få mycket protein eller i ditt fall rejält gröna celler.
pBAD promotorn aktiveras av arabinos precis som i naturen, och ger upphov till transkription av den efterföljande genen för GFP.
Jadå detta operon finns naturligt i E. coli kromosomen. Så när ni tillsatte arabinos aktiverades PBAD promotorn i E. coli kromosomen, så arabinos kunde användas - och den extra PBAD promotorn i er plasmid, vilket gav transkription av er efterföljande GFP gen.
Den starka promotorn PBAD togs från det naturliga operonet och stoppades in i plasmiden, på så vis fås E. coli som kan skapa GFP endast när arabinos finns tillsatt - så ni kan slå på GFP bildningen precis när ni vill genom att bara mata med arabions.
Tack så jättejättemycket verkligen!! Nu förstår jag äntligen hur själva operonet fungerar.
Så det man har gjort i fallet med pGLO plasmiden är att man tagit arabinospromotorn, som aktiveras med arabinos precis som om den hade varit i det naturliga operonet, och sen har man stoppat in GFP-genen efter/i (?) vilket gör att promotorn aktiverar GFP? Är det hela operonet som finns med i pGLO eller endast promotorn (dum fråga kanske men måste bara se så det blir rätt)? Om det är hela operonet, har man tagit bort någon annan gen (exempelvis de strukturella) och bytt ut de med GFP?
Tack så jättejättemycket verkligen!! Nu förstår jag äntligen hur själva operonet fungerar.
Så det man har gjort i fallet med pGLO plasmiden är att man tagit arabinospromotorn, som aktiveras med arabinos precis som om den hade varit i det naturliga operonet, och sen har man stoppat in GFP-genen efter/i (?)
Precis.
vilket gör att promotorn aktiverar GFP?
Promotorn aktiverar transkriptionen av mRNA som kodar för GFP (vilket jag misstänker du menade). GFP proteinets fluorescens aktiveras av ljus.
Är det hela operonet som finns med i pGLO eller endast promotorn (dum fråga kanske men måste bara se så det blir rätt)?
Ja, det är endast promotorn. Resten av operonet behövs inte för att "lura" E. coli att skapa GFP proteinet. Men E. coli bakterien kommer så klart att gilla arabinoset som energi och utnyttja alla sina gener i arabionosoperonet, vilka i E. coli kromosomen.
Om det är hela operonet, har man tagit bort någon annan gen (exempelvis de strukturella) och bytt ut de med GFP
Nej det är bara promotorn. Men det skulle i princip gått att ta bort bara en av de strukturella generna och ersätta den med genen för GFP, men det skulle göra plasmiden onödigt stor (inte en fördel) och plasmiden skulle även innehålla de andra generna från operonet - och dessa påverkar operonet, vilket kan påverka gentranskriptionen från både plasmiden och från E. coli kromosomen (vilket gör det mer komplicerat att få mycket GFP).
mag1 skrev:Tack så jättejättemycket verkligen!! Nu förstår jag äntligen hur själva operonet fungerar.
Så det man har gjort i fallet med pGLO plasmiden är att man tagit arabinospromotorn, som aktiveras med arabinos precis som om den hade varit i det naturliga operonet, och sen har man stoppat in GFP-genen efter/i (?)
Precis.
vilket gör att promotorn aktiverar GFP?
Promotorn aktiverar transkriptionen av mRNA som kodar för GFP (vilket jag misstänker du menade). GFP proteinets fluorescens aktiveras av ljus.
Är det hela operonet som finns med i pGLO eller endast promotorn (dum fråga kanske men måste bara se så det blir rätt)?
Ja, det är endast promotorn. Resten av operonet behövs inte för att "lura" E. coli att skapa GFP proteinet. Men E. coli bakterien kommer så klart att gilla arabinoset som energi och utnyttja alla sina gener i arabionosoperonet, vilka i E. coli kromosomen.
Om det är hela operonet, har man tagit bort någon annan gen (exempelvis de strukturella) och bytt ut de med GFP
Nej det är bara promotorn. Men det skulle i princip gått att ta bort bara en av de strukturella generna och ersätta den med genen för GFP, men det skulle göra plasmiden onödigt stor (inte en fördel) och plasmiden skulle även innehålla de andra generna från operonet - och dessa påverkar operonet, vilket kan påverka gentranskriptionen från både plasmiden och från E. coli kromosomen (vilket gör det mer komplicerat att få mycket GFP).
Okej, men araC genen finns väl fortfarande med i pGLO? (Jag ser att araC inte ingår i operonet så jag formulerade mig lite dumt innan) För som jag förstått det så binder AraC till araO2 och aral1 när det inte finns något arabinos och bildar då en ögla. På det sättet så blockeras promotorn och ingen avläsning sker. Men om araC genen inte finns med längre, hur kontrolleras då promotorn? Stämmer det att araC också finns med i pGLO men det är bara promotorn från själva operonet som flyttats över?
Ja i pGLO finns även araC genen (AraC), bilden nedan visar översiktligt hur generna i plasmiden är ordnade (även riktningen på hur generna transkriberas visas med pilhuvudena). (bilden kommer ifrån ett företag som säljer plasmiden https://www.addgene.org/82500/)
De andra generna är:
promotorn (AraBAD), vita pilen
GFP-genen (GFP-1UAG)
resistens mot ampicillin (AmpR)
Ori - origin of replication (för så att plasmiden kan kopieras av E. coli i samband med celldelning)
F1 Ori - origin of replication (för så att plasmiden kan kopieras och packas in i ett virus, som i sin tur kan infektera E.coli. Behövs vanligtvis inte men finns ofta kvar från tidigare versioner av plasmider)
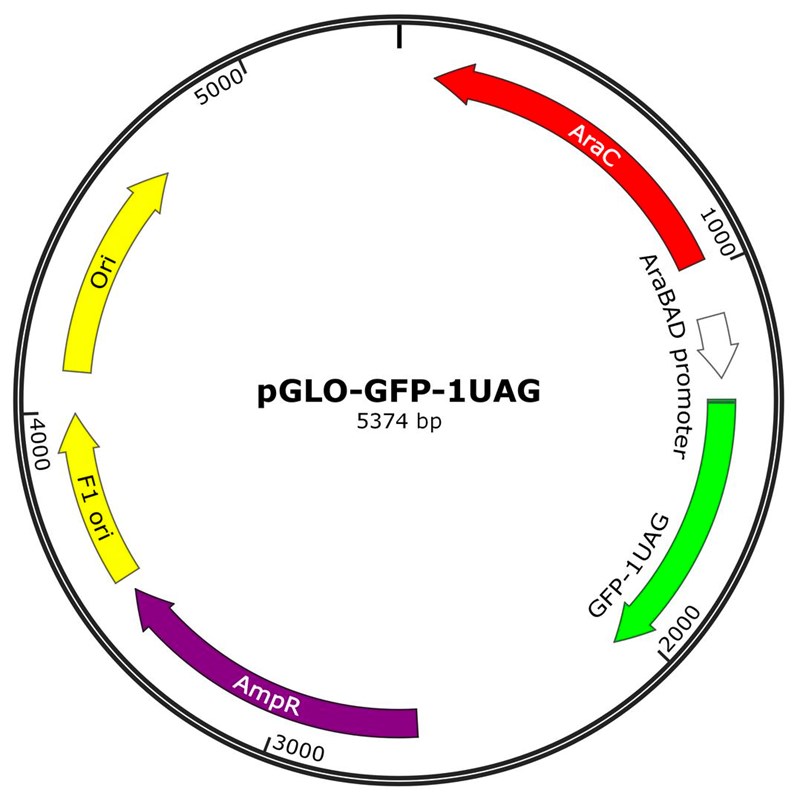
Samtidigt finns ju även araC i E. coli kromosomen, så det bildas även araC protein från denna gen. Men plasmiden kan finnas i mer än en kopia per E. coli cell, så för undvika att det bildas för lite oriC finns denna gen även i plasmiden (så det alltid finns en araC gen per PBAD promotor).
mag1 skrev:Ja i pGLO finns även araC genen (AraC), bilden nedan visar översiktligt hur generna i plasmiden är ordnade (även riktningen på hur generna transkriberas visas med pilhuvudena). (bilden kommer ifrån ett företag som säljer plasmiden https://www.addgene.org/82500/)
De andra generna är:
promotorn (AraBAD), vita pilen
GFP-genen (GFP-1UAG)
resistens mot ampicillin (AmpR)
Ori - origin of replication (för så att plasmiden kan kopieras av E. coli i samband med celldelning)
F1 Ori - origin of replication (för så att plasmiden kan kopieras och packas in i ett virus, som i sin tur kan infektera E.coli. Behövs vanligtvis inte men finns ofta kvar från tidigare versioner av plasmider)
Samtidigt finns ju även araC i E. coli kromosomen, så det bildas även araC protein från denna gen. Men plasmiden kan finnas i mer än en kopia per E. coli cell, så för undvika att det bildas för lite oriC finns denna gen även i plasmiden (så det alltid finns en araC gen per PBAD promotor).
Men stämmer det att när det finns arabinos så binder det till AraC och att de sedan sätter sig vid aral1 och aral2, och på så sätt vecklas öglan ut och RNA-polymeraset kan binda till promotorn? För när jag läste om detta på nätet nu så hittade jag någon källa som specifikt skrev om araC i pGLO (innan har jag bara läst om arabinosoperonet "vanligtvis") och då står det följande:
"araC — gene that encodes the regulatory protein that binds to the pBAD promoter; only when arabinose binds to the AraC protein is the production of GFP switched on. "
Jag hittade även en annan källa som sa likadant.
Det jag inte förstår är alltså om AraC binder till promotorn? När man läser om arabinosoperonet på Wikipedia så verkar det ju inte som att det binder till promotorn, men där står det ju om arabinosoperon generellt. Jag har inte tolkat det som att det är så AraC reglerar transkriptionen. Jag vet inte om de källorna har fel eller om AraC fungerar annorlunda i pGLO plasmiden, att den i plasmiden blockerar för RNA-polymeraset genom att binda till promotorn, men i kromosomen blockerar genom att bilda en ögla (och binda till operatorerna o.s.v.). Det skulle ju i så fall förklara hur den kan blockera RNA-polymeraset utan operatorerna, eftersom att det bara var araC och promotorn som finns i pGLO. Nu blev detta väldigt långt, men sammanfattningsvis;
Fungerar AraC likadant i pGLO som i operonet i kromosomen, eller binder det istället till promotorn i pGLO och på så sätt blockerar transkriptionen?
Det blir djupare och djupare frågor, kul!
Från situationen då glukos finns närvarande så kommer E. coli prioritera att använda favoritkolhydraten glukos (glukos kan gå direkt in i metabolismen och den är anpassad mot glukos), och arabions operonet är då inaktivt. Men när glukoskoncentrationen sjunker och arabinos finns tillgängligt kommer operonet för arabionsmetabolismen aktiveras.
AraC proteinet ser till att inaktivera operonet genom att, som du skrev, bilda en ögla i DNA och gör detta genom att binda som en dimer (=två proteinkedjor som binder till varandra, i detta fall två AraC) till både aral1 och aral2. RNA polymeraset har då ingen chans att komma åt och translatera mRNA.
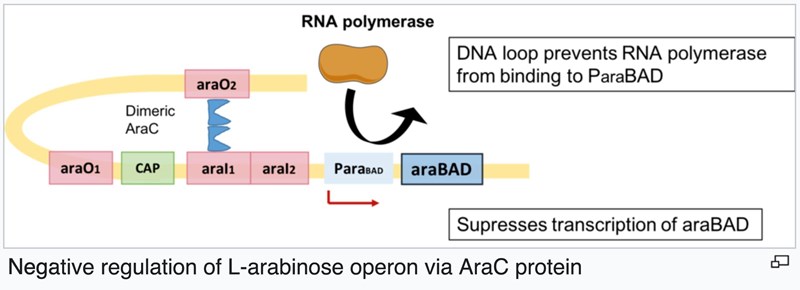
När det finns arabinos finns tillgängligt (och endast lite/inget glukos) binder arabinos till en del av AraC, vilket leder till att AraC proteinet ändrar form lite. I och med detta kan AraC inte binda till araO2 längre och då rättas DNA ut (så att RNA polymeraset har en chans att binda till DNA).
Och med arabinos bundet kommer två kopior (en dimer) av AraC binda till varandra på ett sätt som gör att denna dimer binder till operonets aral1 och aral2, vilket ökar chansen för translation av mRNA från PBAD promotorn - varpå promotorn blir aktiv och translationen av araB/A/D mRNA startar.

Denna bild illustrerar hur hårnålen i DNA bildas utan arabinos genom en typ av AraC-dimer. Och hur AraC interagerar annorlunda med arabionos (grå bollen) bundet och bildar en annan typ av dimer, vilket gör promotorn aktiv.
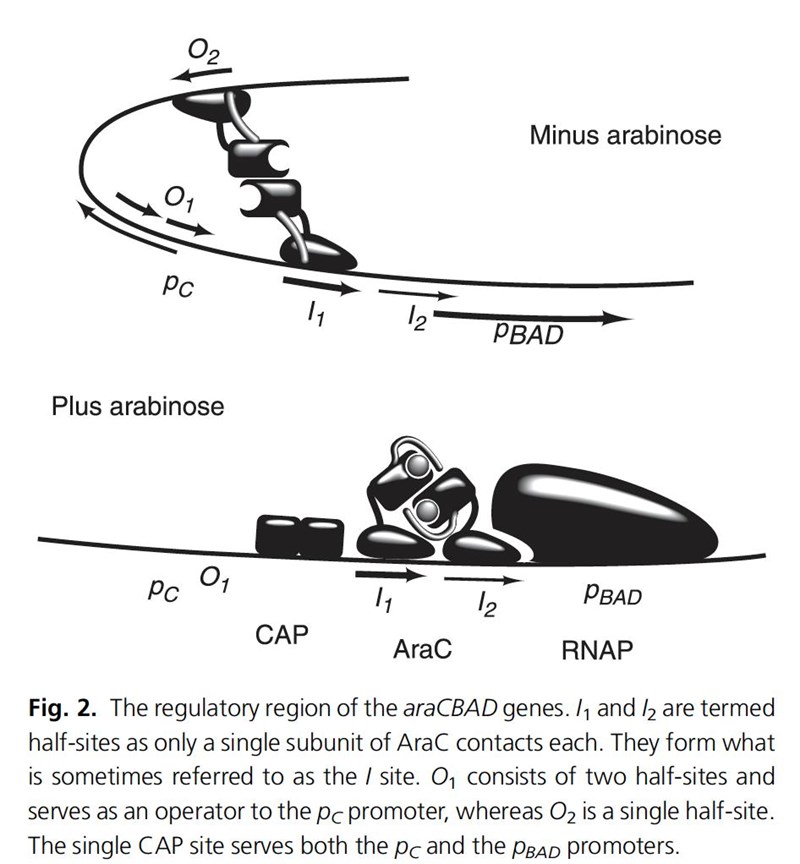
Om vi tittar lite djupare på hur det fungerar i pGLO, så svarade jag för ytligt till att börja med (bra att du frågade vidare). I pGLO plasmiden är det lika dant som i E. coli, d.v.s. operonets reglerande delar är med. Ledsen att jag svarade fel tidigare, men bra att du frågade igen, fick gräva lite själv för jag mindes det som om det endast var delar av operonet (DNA sekvensen för operonet i pGLO är identisk med E. coli sekvensen för operonet, i alla fall för den plasmid jag tittade på från Bio-Rad).
Så ja, i pGLO skapas motsvarande hårnål i DNA när det finns gott om glukos och lite arabinos, vilket gör det omöjligt för RNA polymeraset att binda in. När glukos börjar ta slut och arabions finns ändras detta och PBAD promotorn aktiveras.
Bilderna från wikipedia samt en artikel av Schleif.

