SPR: Varför går grafen under baseline vid regenerering?
Om baseline är nivån då alla ligander är fria, hur kan grafen gå under detta? Det enda jag kan gissa är att en del av liganderna sköljs med vid regenerering, men det låter inte rimligt.
Du är inne på rätt spår. En bra regenerationsbuffert kan vara knepigt att hitta vid SPR.
När baseline sjunker efter regenereringen brukar det bero på att regenerationsbufferten är för aggressiv. Till och med så pass aggressiv att den på chippet bundna liganden dissocierar från chippet och tvättas bort. En mildare regenerationsbuffert behövs istället.
Jaha, okej då var det alltså så. Alla schematiska diagram jag hittar på google visar en liten dip under baseline, vissa inte så djupa men andra väldigt djupa.
Man måste isåfall binda mer ligand innan nästa körning?
Att signalen dippar under baseline och sedan kommer upp till baseline är inget problem, men om signalen ligger kvar under baseline efter regenereringen har du problem.
Teoretiskt skulle det gå att ladda på mer ligand, men det är inte samma parametrar längre, så jämförbarheten mellan körningarna (t.ex. intensiteten, och/eller dissociationskurvorna) kan bli olika, eller inte alls jämförbara.
Det är dock i princip omöjligt att bind in exakt samma mängd. Viss minskning kan gå att leva med, men som jag skrev tidigare - en mildare regenerationsbuffert behövs istället.
Men den kommer väl upp till baseline för att man laddar på nya ligander? Hur annars kommer den upp?
Det kanske inte gör något med färre ligander, men kan det bli "för lite" om man kör om och om med samma chip?
Ta en titt på dessa tre exempel, i det översta fungerar regenereringen optimalt - baseline och signalen från analyten är oförändrade. Då går det att köra på prov efter prov med på samma chip och ligand kombination.
I "Too harsh" tvättas liganden också bort. Då metoden ofta används för att kvantifiera interaktioner med definierade koncentrationer av analyt (för att t.ex. bestämma affinitet) går det inte riktigt att ladda på mer ligand och "kompensera" för att en del tvättas bort - du kan helt enkelt inte veta att du har samma mängd ligand bunden.
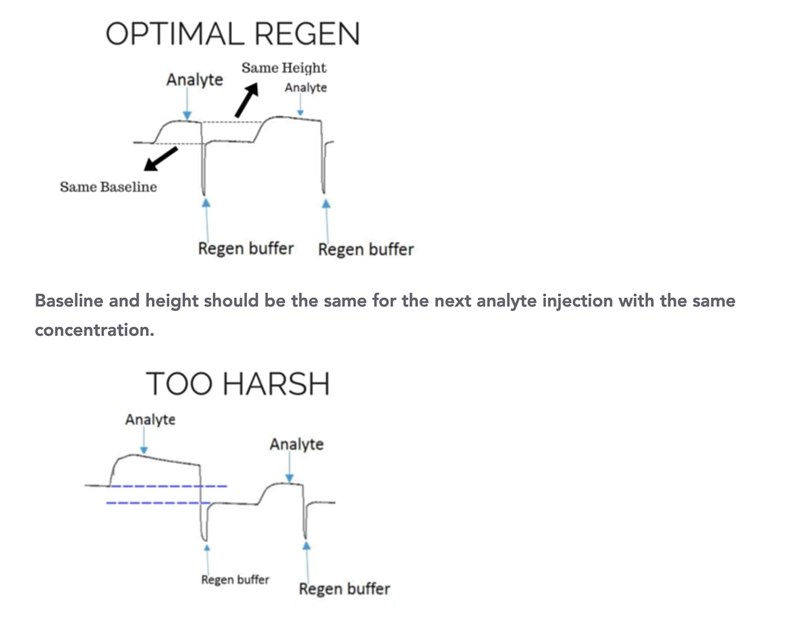
Du vill ha något liknande detta, där baseline är stabil och den ökade intensiteten uppstår av den injicerade analyten och dess koncentration.
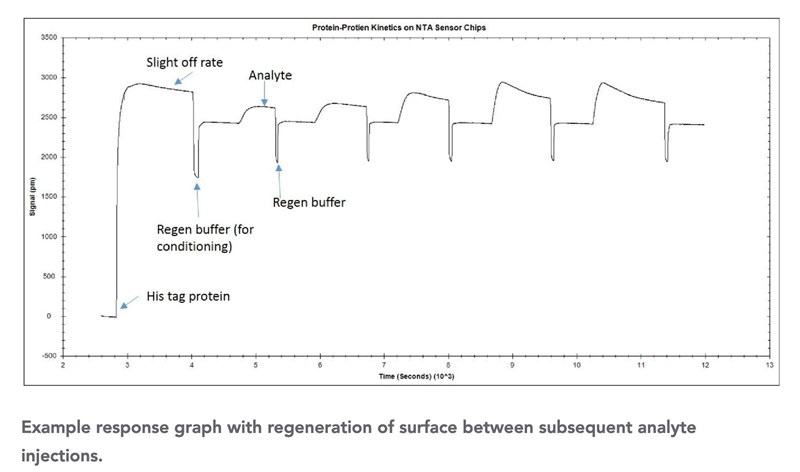
Bilderna och mer information hittade jag hos en leverantör av SPR-instrument.
https://nicoyalife.com/blog/regeneration-buffer-spr-experiment/
Ah, jag förstår nu.
Jag ledde frågan fel egentligen, svaret på min ursprungliga fråga är att varje upp- och nedgång i sensorgrammet inte måste indikera förändring av massan på chippet. Det kan också vara för att lösningen (om den är en annan än standard running buffer) har ett annat brytningsindex, så vid regenerering så orskas dippen inte av att liganderna spolas bort utan för att lösningen är annorlunda helt enkelt.
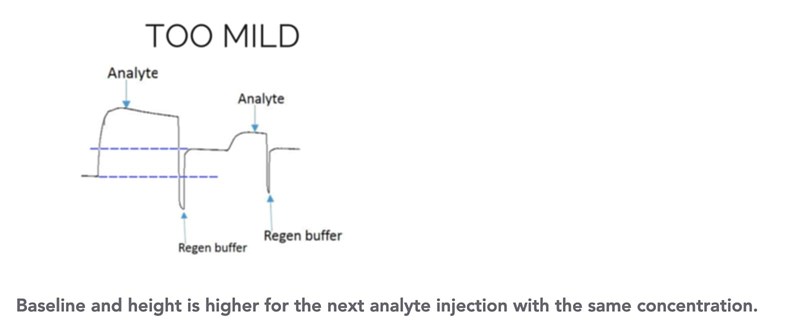
I bilden där det är "too mild" visas alltså när baselinen är högre än innan, det betyder att en del analyt inte tvättats bort?
Qetsiyah skrev:Ah, jag förstår nu.
Jag ledde frågan fel egentligen, svaret på min ursprungliga fråga är att varje upp- och nedgång i sensorgrammet inte måste indikerar förändring av massan på chippet. Det kan också vara för att lösningen (om den är en annan än standard running buffer) har ett annat brytningsindex, så vid regenerering så orskas dippen inte av att liganderna spolas bort utan för att lösningen är annorlunda helt enkelt.
Ja olikheter i lösningarna kan påverka brytning av ljuset kan ge dippar/toppar, som i den idealiserade bilden "example response graphs..." där en rejäl dipp fås, men intensiteten efter ger en stabil baseline.
I bilden där det är "too mild" visas alltså när baselinen är högre än innan, det betyder att en del analyt inte tvättats bort?
Precis, analyten ackumuleras då på chipet.


